Die regelmäßige Durchmischung erinnert zwar an eine ursprüngliche Vielfalt, wie man sie sonst nur in Wildformen findet. Sie verschleiert aber, von welcher Wildform die heutigen Dromedare eigentlich abstammen und damit, wo sie domestiziert wurden.
Burger und ihrem Team gelang es, das aufzuklären. Die Gruppe analysierte bis zu 7.000 Jahre alte DNS aus Knochen der wilden und früh domestizierten Kamele und verglich sie mit den genetischen Profilen moderner weltweiter Dromedarpopulationen. Erstmals war es dadurch möglich, die südöstliche Küste der arabischen Halbinsel als den Ort zu identifizieren, an dem die Nutzung der Kamele als Haustiere begann"
Komplette Pressemitteilung hier
 Algen: Effektive Photosynthetiker
Algen: Effektive Photosynthetiker
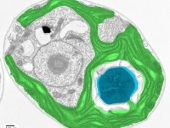
Grünalgen können effektiver Photosynthese betreiben als Nutzpflanzen. Ein Team mit Beteiligung von Forschern um Mark Stitt vom Max-Planck-Institut für Molekulare Pflanzenphysiologie in Potsdam-Golm erklärt die Mechanismen dahinter:
"... Während der Prozess [der Photosynthese] in Pflanzen komplex ist, gelang es den Algen auf recht einfachem Weg die Photosynthese zu verbessern. Sie haben hierfür eine ganz besondere Mikrostruktur, das sogenannte Pyrenoid. Diese Struktur ist in nahezu allen ozeanischen Lebewesen mit Zellkern, die Photosynthese betreiben, vorhanden. So auch in dem Modellorganismus Chlamydomonas reinhardtii, eine im Süßwasser vorkommende Grünalge, die weltweit verbreitet ist. Die Pyrenoide dieses Modelorganismus untersuchte das Wissenschaftsteam genauer. Denn wie genau das Protein Rubisco eigentlich im Pyrenoid verpackt wird, um mit dem hochkonzentrierten CO2 in Kontakt zu kommen, war bisher unklar.
Das Potsdamer Forschungsteam entwickelte hierfür ein Verfahren zur Analyse des Pyrenoids und bestimmte die dort vorhandene Proteinzusammensetzung. Hier fanden sie wie erwartet die Rubisco, aber auch ein Hilfsprotein, welches bei der Strukturanpassung der Rubisco hilft, und ein weiteres, bisher unbekanntes Protein."
Komplette Pressemitteilung hier.
Foto: Moritz Meyer, University of Cambridge
 Wie Fische ihre Augen reparieren
Wie Fische ihre Augen reparieren
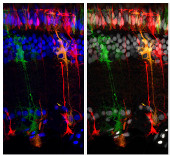
Fische können nicht nur Herz und Flossen nach Verletzungen regenerieren (siehe Laborjournal 5/16), sondern auch die Netzhaut des Auges. Heidelberger Forscher um Joachim Wittbrodt und Lázaro Centanin haben sich den Reparatur-Vorgang auf zellulärer Ebene angeschaut:
"Wie Lázaro Centanin erläutert, umfasst die vollständige Regenerationsreaktion im Fischauge mehrere Schritte. Zuerst beginnen die Müllerzellen, die sich in der Nähe der Verletzung befinden, mit der Zellteilung. Anschließend bilden die dadurch entstandenen Zellhaufen neuronale Cluster, die Vorläuferzellen für die Zelltypen der Netzhaut beinhalten. Im letzten Schritt differenzieren sich diese Vorläuferzellen aus und verwandeln sich in die wiederherzustellenden neuronalen Zellen der Netzhaut. „Wir haben das Potential der Müllerzellen im Medaka-Fisch genutzt, um Faktoren zu testen, die exakt diese Regenerationsreaktion ohne jegliche Art von Verletzung hervorrufen können“, sagt Prof. Wittbrodt. Zum Einsatz kamen dabei verschiedene genetische Faktoren, die entweder für Vermehrung und Wachstum der Zellen von Bedeutung sind oder die in der Zelldifferenzierung eine Rolle spielen. Dabei hat die Arbeitsgruppe um Joachim Wittbrodt ein biologisches Testsystem etabliert, das es erlaubt, die Aktivität beliebiger Gene spezifisch in den Müllerzellen auf ihr regeneratives Potential hin zu testen.
„Wir waren vollkommen überrascht, dass mit dem Gen Atoh7 ein einziger Zelldifferenzierungsfaktor zwei Funktionen erfüllt und für die Regenerationsreaktion am Ende sowohl die Zellteilung als auch die Ausdifferenzierung in die verschiedenen retinalen Zelltypen auslöst“, sagt Katharina Lust, die die Erstautorin der jetzt veröffentlichten Studie ist."
Komplette Pressemitteilung hier.
Foto: Konfokal-Mikroskopiebild eines Schnittes durch die Retina eines Medaka-Fisch. (c) Lust/Wittbrodt









 Algen: Effektive Photosynthetiker
Algen: Effektive Photosynthetiker Wie Fische ihre Augen reparieren
Wie Fische ihre Augen reparieren